Pressemitteilungen Archiv
30.11.2023
Ein Antibiotikum auf Zeitreise
Forschungsteam der Universität Tübingen dreht die Evolution einer bakterientötenden Stoffklasse mithilfe von Computertechnik zurück – Erkenntnisse für die Entwicklung neuer Medikamente
In der modernen Medizin nehmen Antibiotika eine zentrale Rolle bei der Behandlung von bakteriellen Infektionen ein. In der Natur werden sie von Bakterien oder Pilzen hergestellt, die sie selbst ebenfalls zur Abwehr anderer Bakterien nutzen. Anhand einer Gruppe der Glykopeptid-Antibiotika, die wie Teicoplanin und Vancomycin in der Medizin eine wertvolle Reserve gegen vielfach resistente Krankheitserreger bilden, hat ein Forschungsteam die Evolution dieser Stoffklasse untersucht und ein hypothetisches Urantibiotikum rekonstruiert. Dr. Demi Iftime und Dr. Martina Adamek führten das interdisziplinäre Projekt unter Leitung von Professorin Evi Stegmann und Professorin Nadine Ziemert vom Exzellenzcluster „Kontrolle von Mikroorganismen zur Bekämpfung von Infektionen“ der Universität Tübingen durch, unterstützt von Professor Max Cryle und Dr. Mathias Hansen von der Monash University in Australien.
Die Forscherinnen und Forscher ermittelten mithilfe bioinformatischer Methoden, wie die chemische Zusammensetzung des Vorläufers heutiger Glykopeptid-Antibiotika ausgesehen haben könnte und wie dieser durch Evolution umgeformt wurde. Daraus gewinnen sie Erkenntnisse, wie heutige Antibiotika für die medizinische Nutzung weiterentwickelt werden könnten. Ihre Studie wurde in der Fachzeitschrift Nature Communications veröffentlicht.
Ermittlung eines Stammbaums
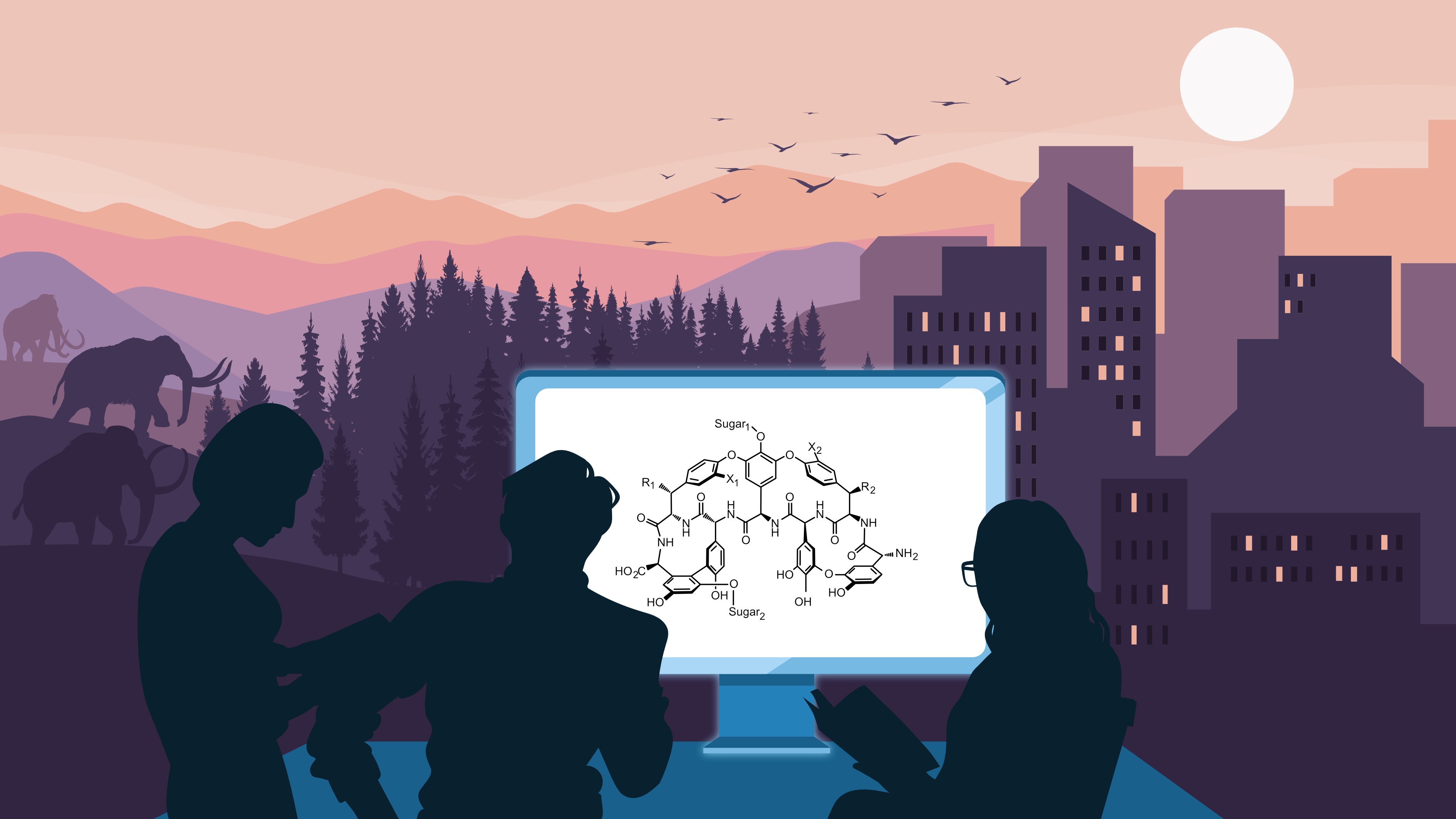
„Antibiotika sind ursprünglich vor allem die Produkte einer stetigen evolutionären Auseinandersetzung zwischen verschiedenen Organismen, die jeweils versuchen, ihre Konkurrenten oder Gegner zu vernichten oder zumindest an der Ausbreitung zu hindern“, erklärt Evi Stegmann. In seiner Studie hat das Forschungsteam Teicoplanin und Vancomycin sowie eine Reihe von ähnlich strukturierten Antibiotika als Ausgangsstoffe herangezogen. Die Naturstoffe können jeweils aus bestimmten Bakterienstämmen isoliert werden. Wie der Name Glykopeptid-Antibiotika beschreibt, bestehen sie chemisch gesehen aus Aminosäuren und Zuckern. Sie lassen Bakterien absterben, indem sie deren Zellwandaufbau verhindern. In dieser Weise wirken Teicoplanin und Vancomycin auch gegen zahlreiche Krankheitserreger des Menschen.
In biologischen Verwandtschaftsanalysen werden meist verschiedene Arten in eine Baumstruktur gestellt, in der die Verzweigungen Auskunft über den Verwandtschaftsgrad geben. „Wir haben in ganz ähnlicher Weise die bekannten Glykopeptid-Antibiotika mit ihrer chemischen Struktur, kodiert über die Gencluster, die ihre Baupläne enthalten, in einen solchen Abstammungsbaum gesetzt“, sagt Ziemert. „Über Computeralgorithmen aus der Bioinformatik lässt sich sozusagen am Stamm des Baumes eine mutmaßliche Urform der Antibiotika errechnen.“ Diesen hypothetischen Vorläufer tauften sie Paleomycin. Das Forschungsteam baute die ermittelten Gene zusammen, welche die Biosynthese von Paleomycin bereits kodiert haben dürften, und ließ ein Bakterium den entsprechenden Stoff produzieren – tatsächlich hatte Paleomycin im Test antibiotische Wirkung. „Es war sehr aufregend, ein solch uraltes Molekül zu erschaffen, als würde man einen Dinosaurier oder ein Wollhaarmammut wieder zum Leben erwecken“, berichtet die Forscherin.
Vereinfachung der Struktur
„Als Ergebnis ist für uns zum einen interessant, dass nach den Berechnungen alle Glykopeptid-Antibiotika von einem einzelnen Vorläufer abstammen“, sagt Stegmann. „Zum anderen ergab sich, dass Paleomycin im Kern des Moleküls eine ähnlich komplexe Peptidstruktur aufweist wie Teicoplanin.“ Bei Vancomycin sei diese Kernstruktur demgegenüber vereinfacht. „Wir gehen davon aus, dass sich diese Vereinfachung erst in der jüngeren Evolution ergeben hat. Die Funktionsweise als Antibiotikum blieb jedoch mit dem gleichen Mechanismus erhalten“, sagt Ziemert. „Für die Bakterien, die solche Antibiotika bilden, können diese sehr nützlich sein. Doch handelt es sich um Stoffe mit einer aufwendigen chemischen Struktur, die das Bakterium viel Energie kosten. Eine Vereinfachung bei gleicher Funktion könnte einen evolutionären Vorteil bieten.“
Dem Stammbaum der verschiedenen Glykopeptid-Antibiotika stellten die Forscherinnen und Forscher einen Stammbaum der diese produzierenden Bakterienstämme gegenüber. Ausgehend von Paleomycin vollzogen sie die Veränderungen in der chemischen Struktur der Antibiotika – beziehungsweise die der unterliegenden Gencluster in den Bakterien – minutiös und Schritt für Schritt nach. Dabei stellten sie fest, welche Schlüsselschritte ungefähr gleichzeitig stattfinden müssen, um ein funktionelles Molekül entstehen zu lassen. Einige dieser Schritte konnten von den Wissenschaftlern in Australien im Labor biochemisch nachvollzogen werden. „Aus dieser Zeitreise erhielten wir tiefgehende Einblicke in die Evolution der Stoffwechselwege der Antibiotikaproduktion in den Bakterien und die Optimierungsstrategien der Natur, die zu den modernen Glykopeptid-Antibiotika führten“, sagt Ziemert. „Dadurch haben wir eine Grundlage, um diese wichtige Antibiotikagruppe mit technischen Methoden weiterzuentwickeln.“
Publikation:
Mathias Hansen, Martina Adamek, Dumitrita Iftime, Daniel Petras, Frauke Schuseil, Stephanie Grond, Evi Stegmann, Max Cryle and Nadine Ziemert: Resurrecting Ancestral Antibiotics: Unveiling the Origins of Modern Lipid II Targeting Glycopeptides. Nature Communications, https://doi.org/10.1038/s41467-023-43451-4
Kontakt:
Universität Tübingen
Interfakultäres Institut für Mikrobiologie und Infektionsmedizin
Exzellenzcluster Kontrolle von Mikroorganismen zur Bekämpfung von Infektionen
Prof. Dr. Nadine Ziemert
Telefon +49 7071 29-78841
nadine.ziemert@uni-tuebingen.de
Prof. Dr. Evi Stegmann
evi.stegmann@uni-tuebingen.de
Pressekontakt:
Eberhard Karls Universität Tübingen
Hochschulkommunikation
Dr. Karl Guido Rijkhoek
Leitung
Janna Eberhardt
Forschungsredakteurin
Telefon +49 7071 29-76788
+49 7071 29-77853
Telefax +49 7071 29-5566
karl.rijkhoek@uni-tuebingen.de
janna.eberhardt@uni-tuebingen.de
Alle Pressemitteilungen der Universität Tübingen